stdClass Object
(
[nazev] => Ústav informatiky a chemie
[adresa_url] =>
[api_hash] =>
[seo_desc] =>
[jazyk] =>
[jednojazycny] =>
[barva] =>
[indexace] => 1
[obrazek] =>
[ga_force] =>
[cookie_force] =>
[secureredirect] =>
[google_verification] => UOa3DCAUaJJ2C3MuUhI9eR1T9ZNzenZfHPQN4wupOE8
[ga_account] => UA-10822215-6
[ga_domain] =>
[ga4_account] => G-VKDBFLKL51
[gtm_id] =>
[gt_code] =>
[kontrola_pred] =>
[omezeni] =>
[pozadi1] =>
[pozadi2] =>
[pozadi3] =>
[pozadi4] =>
[pozadi5] =>
[robots] =>
[htmlheaders] =>
[newurl_domain] => 'lich.vscht.cz'
[newurl_jazyk] => 'cs'
[newurl_akce] => '[cs]'
[newurl_iduzel] =>
[newurl_path] => 8548/43413/28159
[newurl_path_link] => Odkaz na newurlCMS
[iduzel] => 28159
[platne_od] => 31.10.2023 17:04:00
[zmeneno_cas] => 31.10.2023 17:04:23.915555
[zmeneno_uzivatel_jmeno] => Jan Kříž
[canonical_url] =>
[idvazba] => 47447
[cms_time] => 1714123185
[skupina_www] => Array
(
)
[slovnik] => stdClass Object
(
[logo_href] => /
[logo] =>  [logo_mobile_href] => /
[logo_mobile] =>
[logo_mobile_href] => /
[logo_mobile] =>  [google_search] => 001523547858480163194:u-cbn29rzve
[social_fb_odkaz] => https://cs-cz.facebook.com/studuj.bioinformatiku/
[social_tw_odkaz] =>
[social_yt_odkaz] =>
[intranet_odkaz] => //intranet.vscht.cz/
[intranet_text] => Intranet
[mobile_over_nadpis_menu] => Menu
[mobile_over_nadpis_search] => Hledání
[mobile_over_nadpis_jazyky] => Jazyky
[mobile_over_nadpis_login] => Přihlášení
[menu_home] => Domovská stránka
[paticka_mapa_odkaz] => /kontakt
[paticka_budova_a_nadpis] => BUDOVA A
[paticka_budova_a_popis] => Rektor, oddělení komunikace, centrum informačních služeb
[paticka_budova_b_nadpis] => BUDOVA B
[paticka_budova_b_popis] => Děkanáty fakult: FCHT, FTOP, FPBT, FCHI,
pedagogické oddělení, výpočetní centrum, zahraniční oddělení, kvestor
[paticka_budova_c_nadpis] => BUDOVA C
[paticka_budova_c_popis] => Dětský koutek Zkumavka, praktický lékař, Ústav matematiky
[paticka_budova_1_nadpis] => NÁRODNÍ TECHNICKÁ KNIHOVNA
[paticka_budova_1_popis] =>
[paticka_budova_2_nadpis] => STUDENTSKÁ KAVÁRNA CARBON
[paticka_budova_2_popis] =>
[paticka_adresa] => VŠCHT Praha
[google_search] => 001523547858480163194:u-cbn29rzve
[social_fb_odkaz] => https://cs-cz.facebook.com/studuj.bioinformatiku/
[social_tw_odkaz] =>
[social_yt_odkaz] =>
[intranet_odkaz] => //intranet.vscht.cz/
[intranet_text] => Intranet
[mobile_over_nadpis_menu] => Menu
[mobile_over_nadpis_search] => Hledání
[mobile_over_nadpis_jazyky] => Jazyky
[mobile_over_nadpis_login] => Přihlášení
[menu_home] => Domovská stránka
[paticka_mapa_odkaz] => /kontakt
[paticka_budova_a_nadpis] => BUDOVA A
[paticka_budova_a_popis] => Rektor, oddělení komunikace, centrum informačních služeb
[paticka_budova_b_nadpis] => BUDOVA B
[paticka_budova_b_popis] => Děkanáty fakult: FCHT, FTOP, FPBT, FCHI,
pedagogické oddělení, výpočetní centrum, zahraniční oddělení, kvestor
[paticka_budova_c_nadpis] => BUDOVA C
[paticka_budova_c_popis] => Dětský koutek Zkumavka, praktický lékař, Ústav matematiky
[paticka_budova_1_nadpis] => NÁRODNÍ TECHNICKÁ KNIHOVNA
[paticka_budova_1_popis] =>
[paticka_budova_2_nadpis] => STUDENTSKÁ KAVÁRNA CARBON
[paticka_budova_2_popis] =>
[paticka_adresa] => VŠCHT Praha
Technická 5
166 28 Praha 6 – Dejvice
IČ: 60461373
DIČ: CZ60461373
Datová schránka: sp4j9ch
Copyright VŠCHT Praha
Za informace odpovídá Oddělení komunikace, technický správce Výpočetní centrum
[paticka_odkaz_mail] => mailto:lich@vscht.cz
[zobraz_desktop_verzi] => Zobrazit plnou verzi
[social_fb_title] => Facebook Bioinformatika
[social_tw_title] =>
[social_yt_title] =>
[aktualizovano] => Aktualizováno
[autor] => Autor
[drobecky] => Nacházíte se: VŠCHT Praha – FCHT – LICH
[preloader] => Prosím počkejte chvíli...
[more_info] =>
[zobraz_mobilni_verzi] =>
[nepodporovany_prohlizec] =>
[social_in_odkaz] =>
[hledani_nadpis] => hledání
[hledani_nenalezeno] => Nenalezeno...
[hledani_vyhledat_google] => vyhledat pomocí Google
[social_li_odkaz] =>
)
[poduzel] => stdClass Object
(
[28161] => stdClass Object
(
[obsah] =>
[poduzel] => stdClass Object
(
[28167] => stdClass Object
(
[obsah] =>
[iduzel] => 28167
[canonical_url] => //lich.vscht.cz
[skupina_www] => Array
(
)
[url] =>
[sablona] => stdClass Object
(
[class] =>
[html] =>
[css] =>
[js] =>
[autonomni] =>
)
)
[28165] => stdClass Object
(
[obsah] =>
[iduzel] => 28165
[canonical_url] => //lich.vscht.cz
[skupina_www] => Array
(
)
[url] =>
[sablona] => stdClass Object
(
[class] =>
[html] =>
[css] =>
[js] =>
[autonomni] =>
)
)
[28166] => stdClass Object
(
[obsah] =>
[iduzel] => 28166
[canonical_url] => //lich.vscht.cz
[skupina_www] => Array
(
)
[url] =>
[sablona] => stdClass Object
(
[class] =>
[html] =>
[css] =>
[js] =>
[autonomni] =>
)
)
)
[iduzel] => 28161
[canonical_url] =>
[skupina_www] => Array
(
)
[url] =>
[sablona] => stdClass Object
(
[class] =>
[html] =>
[css] =>
[js] =>
[autonomni] =>
)
)
[28162] => stdClass Object
(
[obsah] =>
[poduzel] => stdClass Object
(
[28301] => stdClass Object
(
[nazev] => Cheminformatika
[seo_title] => Cheminformatika
[seo_desc] =>
[autor] =>
[autor_email] =>
[obsah] =>
Vedoucí skupiny
prof. Mgr. Daniel Svozil, Ph.D. e 220 442 244 d B1320
Členové týmuVýzkumní pracovníci Ph.D. studenti PublikaceSoftware |
Cheminformatika se zabývá použitím výpočetních technik pro pochopení vztahů mezi biologickou aktivitou a strukturou organické sloučeniny. Cheminformatika je mezioborová disciplína kloubící dohromady chemii, statistiku, informatiku a molekulární biologii.
V naší skupině se zabýváme návrhem a analýzou struktur organických sloučenin za účelem nalezení látek vykazujících definovaný biologický efekt. Úzce spolupracujeme s Oddělením buněčné diferenciace Dr. P. Bartůňka z Ústavu molekulární genetiky AV ČR. V rámci této spolupráce se zabýváme výzkumem úlohy jaderných receptorů s cílem prohloubit naše znalosti o příčinách vzniku nádorových onemocnění a o možnostech jejich prevence a léčby.
Oddělení buněčné diferenciace provozuje Národní infrastrukturu chemické biologie CZ-OPENSCREEN, která je národním uzlem evropské infrastruktury EU-OPENSCREEN. Naše skupina je, jako jeden ze členů této infrastruktury, zodpovědná za oblast cheminformatiky a analýzy dat. Zapojení v infrastruktuře chemické biologie nám zajištuje přístup k zajímavým evropským projektům a trvalý zdroj financování našich výzkumných aktivit. |
Od akademického roku 2014/2015 provozujeme bakalářský a magisterský program "Bioinformatika". V akademickém roce 2019/2020 pak k nabídce přibyl též stejnojmenný doktorský program. Abychom studentům nabídli co nejkvalitnější vzdělání, spojili jsme se při zajišťování oboru s našimi kolegy z dalších akademických pracovišť.
- Předměty přírodovědného základu jsou vyučovány zde na VŠCHT.
- Informatiku zajišťuje FIT ČVUT.
- Specializované bioinformatické přednášky v magisterském studiu zajišťují bioinformatické laboratoře působící na ÚMG a ÚOCHB AV ČR.
Přednášející z těchto pracovišť též vypisují bakalářské, diplomové a dizertační práce, což nám umožňuje nabízet témata z mnoha různých oblastí. Řešené práce pokrývají především problematiku z
- bioinformatiky
- systémové biologie
- cheminformatiky
- počítačového návrhu léčiv
- molekulového modelování biologických systémů
Vedoucí skupiny
doc. Ing. Filip Lankaš, Ph.D. e 220 444 392 d Z12b
Členové týmu
Mgr. Tomáš Dršata, Ph.D. Ing. Hana Dohnalová Ing. Eva Matoušková Bc. Martina Zoubková Oleksandra Shumilina
Hledáme nové kolegy na všech stupních studia.
Publikace
Výuka |
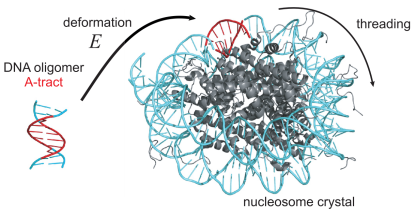
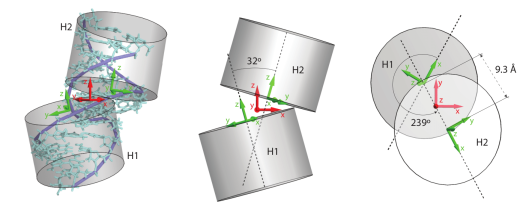
Naše výzkumná skupina se zaměřuje na teorii a počítačové modelování struktury, dynamiky a mechanických vlastností nukleových kyselin. Molekuly DNA a RNA modelujeme na různých délkových a časových škálách, parametry modelů pak stanovujeme z dat získaných rozsáhlými simulacemi molekulové dynamiky. Výsledky aplikujeme na problémy z oblasti molekulární biologie, biofyziky a návrhu umělých molekulárních nanostruktur. Skupina disponuje výpočetní kapacitou pro rozsáhlé simulace i zpracování dat. Jsme rovněž zapojeni do společných projektů s českými a zahraničními vědeckými pracovišti.
Zabýváme se dvěma okruhy témat.
Sekvenčné závislá struktura a elasticita DNA. Detailní prostorová struktura a mechanická tuhost (elasticita, flexibilita) dvoušroubovice DNA závisí na sekvenci bazí, jimiž je tvořena. Tuto vlastnost využívají mnohé proteiny (např. transkripční faktory) pro sekvenčně specifickou vazbu k DNA - protein se preferenčně váže k takové sekvenci, jejích prostorová konfigurace a flexibilita jsou příznivé pro tvorbu komplexu. Naším cílem je vyvinout spolehlivé modely, které přiřadí dané sekvenci její tvar a flexibilitu. Tuto informaci lze pak využít pro predikci prostorové struktury genomu, vazebných míst proteinů a malých molekul i v procesu návrhu nanostruktur DNA. Samostatný výzam má pak stanovení vlastností DNA poškozené následkem UV záření.
Dynamika a mechanické vlastnosti strukturních motivů RNA. Molekuly RNA jsou strukturně velmi bohaté - kromě dvoušroubovice se sbalují do různých nehelikálních strukturních motivů, které příroda opakovaně využívá. Např. v ribosomu, makromolekulárním komplexu syntetizujícím proteiny, funkčně spolupracují rigidní i flexibilní motivy. Tyto motivy tvoří také stavební prvky umělých nanostruktur, jejichž návrh i aplikace se v současnosti prudce rozvíjejí. Výhodou nanostruktur RNA je možnost jejich syntézy přímo v buňce, bez nutnosti přechodu přes buněčnou membránu. Našim cílem je vyvinout vhodné modely a stanovit jejich parametry tak, abychom popsali strukturní dynamiku a mechanické vlastnosti důležitých motivů. To přispěje jednak k pochopení biologické funkce jejich komplexů, jako je ribosom, jednak k racionalizaci návrhu nanostruktur RNA.
|
Nemáte přístup k obsahu stránky.
Zkontrolujte, zda jste v síti VŠCHT Praha, nebo se přihlaste (v pravém horním rohu stránek).
[urlnadstranka] => [iduzel] => 10947 [canonical_url] => [skupina_www] => Array ( ) [url] => /[error403] [sablona] => stdClass Object ( [class] => stranka_ikona [html] => [css] => [js] => [autonomni] => 1 ) ) [1485] => stdClass Object ( [nazev] => Stránka nenalezena [seo_title] => Stránka nenalezena (chyba 404) [seo_desc] => Chyba 404 [autor] => [autor_email] => [obsah] =>Chyba 404
Požadovaná stránka se na webu (již) nenachází. Kontaktuje prosím webmastera a upozorněte jej na chybu.
Pokud jste změnili jazyk stránek, je možné, že požadovaná stránka v překladu neexistuje. Pro pokračování prosím klikněte na home.
Děkujeme!
[urlnadstranka] => [ogobrazek] => [pozadi] => [iduzel] => 1485 [canonical_url] => [skupina_www] => Array ( ) [url] => /[error404] [sablona] => stdClass Object ( [class] => stranka [html] => [css] => [js] => [autonomni] => 1 ) ) [28175] => stdClass Object ( [nazev] => O ústavu [seo_title] => Úvod [seo_desc] => [autor] => [autor_email] => [obsah] =>V roce 2002 byla na VŠCHT Praha založena, iniciativou Dr. Miloslava Niče, Laboratoř informatiky a chemie. Zpočátku se Laboratoř soustředila na odborné elektronické publikování v oblasti chemie a garantovala studijní obor “Informatika a chemie”. V září 2010 došlo ke změně na pozici vedoucího, kdy Dr. M. Niče vystřídal doc. Daniel Svozil. S jeho příchodem se zaměření laboratoře změnilo a nyní se pracoviště zabývá výzkumem v oborech bioinformatika, cheminformatika, počítačový návrh léčiv a molekulové modelování. To se odrazilo i v akreditaci Bc. a Mgr. programu “Bioinformatika”, který je na VŠCHT vyučován od akademického roku 2014/2015. V listopadu 2017 byla Laboratoř transformována na Ústav informatiky a chemie. V roce 2019/2020 pak byla zahájena výuka v doktorském studijním programu "Bioinformatika".
[urlnadstranka] => [ogobrazek] => [pozadi] => [iduzel] => 28175 [canonical_url] => [skupina_www] => Array ( ) [url] => /home [sablona] => stdClass Object ( [class] => stranka [html] => [css] => [js] => [autonomni] => 1 ) ) [28291] => stdClass Object ( [nazev] => [seo_title] => Lidé [seo_desc] => [autor] => [autor_email] => [obsah] =>Akademičtí pracovníci
 |
vedoucí ústavu |
b daniel.svozil at vscht.cz | e 220 442 244 | d B1320 |
 |
tajemník ústavu |
b petr.cech at vscht.cz | e 220 443 366 | d B1319 |
 |
PZVT |
b jiri.znamenacek at vscht.cz | e 220 442 041 | d B1316 |
 |
referent BOZP |
b filip.lankas at vscht.cz | e 220 442 074 | d B1318 |
 |
Ing. Ivan Čmelo, Ph.D. | b ivan.cmelo at vscht.cz | e 220 444 379 | d B1318 |
 |
Ing. Jiří Jirát, Ph.D. | b jiri.jirat at vscht.cz | e 220 444 393 | d A320B |
| Mgr. Michal Kolář, Ph.D. | b michal.kolar at vscht.cz | e 220 442 080 | d B1314 | |
| Mgr. Mariia Matveieva, Ph.D. | b mariia.matveieva at vscht.cz | e 220 442 075 | d B1317 | |
| Mgr. Jan Pačes, Ph.D. | b jan.paces at vscht.cz | e 220 442 080 | d B1314 | |
 |
Ing. Martin Šícho, Ph.D. | b martin.sicho at vscht.cz | ||
 |
Ing. Milan Voršilák, Ph.D. | b milan.vorsilak at vscht.cz |
Ph.D. studenti
 |
M.Sc. Isabel Agea | b Maria.Isabel.Agea.Lorente at vscht.cz | ||
| Ing. Kamila Clarová | b kamila.clarova at vscht.cz | e 220 442 081 | d B1317 | |
 |
M.Sc. Wim Dehaen | b wim.dehaen at vscht.cz | e 220 442 014 | d B1316 |
 |
Ing. Hana Dohnalová | b hana.dohnalova at vscht.cz | e 220 442 014 | d B1316 |
| Ing. Valeriia Fil | b valeriia.fil at vscht.cz | e 220 442 014 | d B1316 | |
| Ing. Eva Matoušková | b eva.matouskova at vscht.cz | e 220 442 014 | d B1316 | |
| Ing. František Pešina | b frantisek.pesina at vscht.cz | e 220 442 014 | d B1316 | |
| Ing. David Příhoda | b david.prihoda at vscht.cz | e 220 442 014 | d B1316 |
DATA
stdClass Object
(
[nazev] => Cheminformatika
[seo_title] => Cheminformatika
[seo_desc] =>
[autor] =>
[autor_email] =>
[obsah] =>
Vedoucí skupiny
prof. Mgr. Daniel Svozil, Ph.D. e 220 442 244 d B1320
Členové týmuVýzkumní pracovníci Ph.D. studenti PublikaceSoftware |
Cheminformatika se zabývá použitím výpočetních technik pro pochopení vztahů mezi biologickou aktivitou a strukturou organické sloučeniny. Cheminformatika je mezioborová disciplína kloubící dohromady chemii, statistiku, informatiku a molekulární biologii.
V naší skupině se zabýváme návrhem a analýzou struktur organických sloučenin za účelem nalezení látek vykazujících definovaný biologický efekt. Úzce spolupracujeme s Oddělením buněčné diferenciace Dr. P. Bartůňka z Ústavu molekulární genetiky AV ČR. V rámci této spolupráce se zabýváme výzkumem úlohy jaderných receptorů s cílem prohloubit naše znalosti o příčinách vzniku nádorových onemocnění a o možnostech jejich prevence a léčby.
Oddělení buněčné diferenciace provozuje Národní infrastrukturu chemické biologie CZ-OPENSCREEN, která je národním uzlem evropské infrastruktury EU-OPENSCREEN. Naše skupina je, jako jeden ze členů této infrastruktury, zodpovědná za oblast cheminformatiky a analýzy dat. Zapojení v infrastruktuře chemické biologie nám zajištuje přístup k zajímavým evropským projektům a trvalý zdroj financování našich výzkumných aktivit. |
Tato sekce obsahuje seznam prací publikovaných v rámci výzkumné skupiny Cheminformatika. Publikace jednotlivých členů výzkumné skupiny Cheminformatika je možné nalézt v jejich ORCID záznamech.
| Jméno a příjmení | ID |
| Daniel Svozil |
ORCID: 0000-0003-2577-5163 ResearcherID: D-4407-2009 Scopus ID: 7801389117 |
| Petr Čech | ORCID: 0000-0003-4605-6029 |
| Ivan Čmelo | ORCID: 0000-0001-7787-8653 |
| Martin Šícho | ORCID: 0000-0002-8771-1731 |
| Milan Voršilák | ORCID: 0000-0002-8923-1627 |
| Isabel Agea | ORCID: 0000-0002-3017-7742 |
| Paola Staffiere | ORCID: 0000-0003-1961-7302 |
| David Příhoda | ORCID: 0000-0003-0083-7428 |
| Kamila Clarová | ORCID: 0000-0002-3641-2571 |
| Wim Dehaen | ORCID: 0000-0001-6979-5508 |
| František Pešina | ORCID: 0000-0002-8116-6891 |
2021
42. Wilm A, Norinder U, Agea MI, de Bruyn Kops C, Stork C, Kühnl J, Kirchmair J. Skin Doctor CP: Conformal Prediction of the Skin Sensitization Potential of Small Organic Molecules. Chem Res Toxicol. 2021 Feb 15;34(2):330-344. DOI: 10.1021/acs.chemrestox.0c00253
41. de Bruyn Kops C, Šícho M, Mazzolari A, Kirchmair J. GLORYx: Prediction of the Metabolites Resulting from Phase 1 and Phase 2 Biotransformations of Xenobiotics. Chem Res Toxicol. 2021 Feb 15;34(2):286-299. DOI: 10.1021/acs.chemrestox.0c00224
40. Čmelo I, Voršilák M, Svozil D. Profiling and analysis of chemical compounds using pointwise mutual information. J Cheminform. 2021 Jan 10;13(1):3. DOI: 10.1186/s13321-020-00483-y
2020
39. Prihoda D, Maritz JM, Klempir O, Dzamba D, Woelk CH, Hazuda DJ, Bitton DA, Hannigan GD. The application potential of machine learning and genomics for understanding natural product diversity, chemistry, and therapeutic translatability. Nat Prod Rep. 2020 Nov 27. DOI: 10.1039/d0np00055h
38. Jurásek B., Čmelo I., Svoboda J. Čejka J., Svozil D., Kuchař M. New psychoactive substances on dark web markets: from deal solicitation to forensic analysis of purchased substances. Drug Testing and Analysis 13 (1) 156-168 2020. DOI: 10.1002/dta.2901
37. Jurásek B., Bartůněk V., Huber Š., Fagan P., Setnička V., Králík F., Dehaen W., Svozil D., Kuchař M. Can X-Ray Powder Diffraction Be a Suitable Forensic Method for Illicit Drug Identification? Frontiers in Chemistry 8:499 2020. DOI: 10.3389/fchem.2020.00499
36. Cortés-Ciriano I., Škuta C., Bender A., Svozil D. QSAR-derived affinity fingerprints (part 2): modeling performance for potency prediction. Journal of Cheminformatics 12:41 2020. DOI: 10.1186/s13321-020-00444-5
35. Škuta C., Cortés-Ciriano I., Dehaen W., Kříž P., van Westen G. J. P., Tetko I. V., Bender A., Svozil D. QSAR-derived affinity fingerprints (part 1): fingerprint construction and modeling performance for similarity searching, bioactivity classification and scaffold hopping. Journal of Cheminformatics 12:39 2020. DOI: 10.1186/s13321-020-00443-6
34. Voršilák M., Kolář M., Čmelo I., Svozil D. SYBA: Bayesian estimation of synthetic accessibility of organic compounds. Journal of Cheminformatics 12:35 2020. DOI: 10.1186/s13321-020-00439-2
33. Stork C., Embruch B.,Šícho M., de Bruyn Kops C., Chen Y., Svozil D., Kirchmair J. NERDD: A web portal providing access to in silico tools for drug discovery. Bioinformatics 36 (4) 1291-1292 2020. DOI: 10.1093/bioinformatics/btz695
2019
32. Hannigan GD, Prihoda D, Palicka A, Soukup J, Klempir O, Rampula L, Durcak J, Wurst M, Kotowski J, Chang D, Wang R, Piizzi G, Temesi G, Hazuda DJ, Woelk CH, Bitton DA. A deep learning genome-mining strategy for biosynthetic gene cluster prediction. Nucleic Acids Res. 2019 Oct 10;47(18):e110. DOI: 10.1093/nar/gkz654
31. Šícho M., Stork C., Mazzolari A., de Bruyn Kops C., Pedretti A., Testa B., Vistoli G., Svozil D., Kirchmair J. FAME 3: Predicting the Sites of Metabolism in Synthetic Compounds and Natural Products for Phase 1 and Phase 2 Metabolic Enzymes. Journal of Chemical Information and Modelling 59 (8) 3400-3412 2019. DOI: 10.1021/acs.jcim.9b00376
30. de Bruyn Kops C., Stork C., Šícho M., Kochev N., Svozil D., Jeliazkova N., Kirchmair J. GLORY: Generator of the Structures of Likely Cytochrome P450 Metabolites Based on Predicted Sites of Metabolism. Frontiers in Chemistry 7:402 2019. DOI: 10.3389/fchem.2019.00402
29. Stork C, Chen Y, Šícho M, Kirchmair J. Hit Dexter 2.0: Machine-Learning Models for the Prediction of Frequent Hitters. J Chem Inf Model. 2019 Mar 25;59(3):1030-1043. DOI: 10.1021/acs.jcim.8b00677
2018
28. Voršilák M., Svozil D., Comment on "The power metric: a new statistically robust enrichment-type metric for virtual screening applications with early recovery capability". Journal of Cheminformatics 10:13 2018. DOI: 10.1186/s13321-018-0267-x
27. Schneider B., Božíková P., Nečasová I., Čech P., Svozil D., Černý J., A DNA structural alphabet provides new insight into DNA flexibility. Acta Cryst. D 74 52-64 2018. DOI: 10.1107/S2059798318000050
2017
- V listopadu 2017 vyšlo zvláštní číslo Chemických listů věnované počítačovému návrhu léčiv. Autoři deseti článků pochází z našeho pracoviště a z Ústavu molekulární genetiky AV ČR. Články jsou v českém jazyce, zde je seznam příspěvků, na kterých jsme se autorsky podíleli:
- Úvodník: Svozil D., Bartůněk P., Computer Design of Drugs - Revaluated or Usable Helpers? Chemické listy 111 (11) 709-709 2017.
- Jirát J., Svozil D., Linear Representation of Chemical Structures. Chemické listy 111 (11) 710-715 2017.
- Novotný J., Svozil D., Characterization and Similarity Measurement of Molecules Using Molecular Descriptors? Chemické listy 111 (11) 716-723 2017.
- Čmelo I., Svozil D., Chemical Space. Chemické listy 111 (11) 724-730 2017.
- Svozil D., Virtual Screening. Chemické listy 111 (11) 738-746 2017.
- Škuta C., Svozil D., QSAR – Modelling of Quantitative Relations between Structure and Activity of Chemical Compounds. Chemické listy 111 (11) 747-753 2017.
- Šícho M., Svozil D., Molecular Docking as a Tool to Virtually Develop Drugs. Chemické listy 111 (11) 754-759 2017.
- Voršilák M., Svozil D., Estimation of Synthetic Accessibility during Computational Drug Design. Chemické listy 111 (11) 760-765 2017.
26. Schneider B., Božíková P., Čech P., Svozil D., Černý J., A DNA Structural Alphabet Distinguishes Structural Features of DNA Bound to Regulatory Proteins and in the Nucleosome Core Particle. Genes 8 (10) 278 2017. DOI: 10.3390/genes8100278
25. Šícho M., de Bruyn Kops C., Stork C., Svozil D., Kirchmair J., FAME 2: Simple and Effective Machine Learning Model of Cytochrome P450 Regioselectivity. Journal of Chemical Information and Modelling 57 (8) 1832-1846 2017. DOI: 10.1021/acs.jcim.7b00250
24. Škuta C., Popr M. Muller T., Jindřich J., Kahle M., Sedlák D., Svozil D., Bartůněk P., Probes & Drugs portal: an interactive, open data resource for chemical biology. Nature Methods 14 (8) 758-759 2017. DOI: 10.1038/nmeth.4365
23. Voršilák M., Svozil D., Nonpher: computational method for design of hard-to-synthesize structures. Journal of Cheminformatics 9:20 2017. DOI: 10.1186/s13321-017-0206-2
2015
22. Čech P., Hoksza D., Svozil D.: MultiSETTER: web server for multiple RNA structure comparison. BMC Bioinformatics 16 : 253 2015. DOI: 10.1186/s12859-015-0696-8
21. Hoksza D., Svozil D.: Multiple 3D RNA structure superposition using neighbor joining. IEEE IEEE/ACM Transactions on Computational Biology and Bioinformatics 12 (3): 520-530 2015. DOI: 10.1109/TCBB.2014.2351810
2014
20. Škuta C., Bartůněk P., Svozil D.: InCHlib - interactive cluster heatmap for web applications. Journal of Cheminformatics 6 : 44 2014. DOI: 10.1186/s13321-014-0044-4
19. Hoksza D., Škoda P., Voršilák M., Svozil D.: Molpher: a software framework for systematic chemical space exploration. Journal of Cheminformatics 6 : 7 2014. DOI: 10.1186/1758-2946-6-7
18. Schneider B., Černý J., Svozil D., Čech P., Gelly J.-P., de Brevern A. G.: Bioinformatic analysis of the protein/DNA interface. Nucleic Acids Reasearch 42 (5): 3381-3394 2014. DOI: 10.1093/nar/gkt1273
2013
17. Hoksza D., Szepe P., Svozil D., MultiSETTER - Multiple RNA Structure Similarity Algorithm. 8th Brazilian Symposium on Bioinformatics (BSB) 2013, Recife, Brazil, ISBN 978-3-319-02623-7, pp. 59-70, Advances in Bioinformatics and Computational Biology, LNCS 8213, Springer. DOI: 10.1007/978-3-319-02624-4_6
16. Čech P., Kukal J., Černý J., Schneider B., Svozil D.: Automatic workflow for the classification of local DNA conformations. BMC Bioinformatics 14: 205 2013. DOI: 10.1186/1471-2105-14-205
15. Mládek A., Krepl M., Svozil D., Čech P., Otyepka M., Banáš P., Zgarbová M., Jurečka P., Šponer J.: Benchmark quantum-chemical calculations on a complete set of rotameric families of the DNA sugar-phosphate backbone and their comparison with modern density functional theory. Physical Chemistry Chemical Physics 15 (19): 7295-7310 2013. DOI: 10.1039/C3CP44383C
14. Jirát J., Čech P., Znamenáček J., Šimek M., Škuta C., Vaněk T., Dibuszová E., Nic M., Svozil D..: Developing and Implementing a Combined Chemistry and Informatics Curriculum for Undergraduate and Graduate Students in the Czech Republic. Journal of Chemical Education 90 (3): 315-319 2013. DOI: 10.1021/ed3001446
2012
13. Šponer J., Mládek A., Šponer J. E., Svozil D., Zgarbová M., Banáš P., Jurečka P., Otyepka M., The DNA and RNA sugar–phosphate backbone emerges as the key player. An overview of quantum-chemical, structural biology and simulation studies. Physical Chemistry Chemical Physics 14 (44): 15257-15277 2012. DOI: 10.1039/c2cp41987d
12. Banáš P., Mládek A., Otyepka M., Zgarbová M., Jurečka P., Svozil D., Lankaš F., Šponer J., Can We Accurately Describe the Structure of Adenine Tracts in B-DNA? Reference Quantum-Chemical Computations Reveal Overstabilization of Stacking by Molecular Mechanics. Journal of Chemical Theory and Computation 8 (7): 2448-2460 2012. DOI: 10.1021/ct3001238
11. Šponer J., Morgado C. A., Svozil D.: Comment on "Computational Model for Predicting Experimental RNA and DNA Nearest-Neighbor Free Energy Rankings". Journal of Physical Chemistry B 116 (28): 8331-8332. DOI: 10.1021/jp300659f
10. Morgado C. A., Svozil D., Turner D. H., Šponer J.: Understanding the role of base stacking in nucleic acids. MD and QM analysis of tandem GA base pairs in RNA duplexes. Physical Chemistry Chemical Physics 14 (36): 12580-12591 2012. DOI: 10.1039/C2CP40556C
9. Čech P., Svozil D., Hoksza D., SETTER: web server for RNA structure comparison. Nucleic Acids Research W1: W42-W48 2012. DOI: 10.1093/nar/gks560
8. Hoksza D., Svozil D., Efficient RNA pairwise structure comparison by SETTER method. Bioinformatics 28 (14): 1858-1864 2012. DOI: 10.1093/bioinformatics/bts301
2011
7. Čech P., Svozil D., mmView: a web-based viewer of the mmCIF format. BMC Research Notes 4:121 2011. DOI: 10.1186/1756-0500-4-121
6. Hoksza D., Svozil D., Exploration of Chemical Space by Molecular Morphing. IEEE International Conference on Bioinformatics & Bioengineering (BIBE) 2011, Taiwan, ISBN 978-0-7695-4391-8, pp. 201-208. DOI: 10.1109/BIBE.2011.38
5. Hoksza D., Svozil D., SETTER - RNA SEcondary sTructure-based TERtiary Structure Similarity Algorithm. 7th International Symposium on Bioinformatics Research and Applications (ISBRA) 2011, Central South University, China, ISBN 978-3-642-21259-8, pp. 37-49, LNBI 6674, Springer. DOI: 10.1007/978-3-642-21260-4_8
2010
4. Svozil D., Multilayer Neural Networks in Bioinformatics, in Artificial Intelligence and Congnitive Science II, V. Kvasnicka, J. Pospichal (Eds.), Publishing House of Slovak Technical University, Bratislava, 2010. Book chapter
3. Mládek A., Šponer J. E., Jurečka P., Banáš P., Otyepka M., Svozil D., Šponer J., Conformational Energies of DNA Sugar-Phosphate Backbone: Reference QM Calculations and a Comparison with Density Functional Theory and Molecular Mechanics. Journal of Chemical Theory and Computation 12 (6): 3817-3835 2010. DOI: 10.1021/ct1004593
2. Morgado C. A., Jurečka P., Svozil D., Hobza P., Šponer J., Reference MP2/CBS and CCSD(T) quantum-chemical calculations on stacked adenine dimers. Comparison with DFT-D, MP2.5, SCS(MI)-MP2, M06-2X, CBS(SCS-D) and force field descriptions. Physical Chemistry Chemical Physics 12 (14): 3522-3534 2010. DOI: 10.1039/b924461a
1. Svozil D., Hobza P., Šponer J., Comparison of Intrinsic Stacking Energies of Ten Unique Dinucleotide Steps in A-RNA and B-DNA Duplexes. Can We Determine Correct Order of Stability by Quantum-Chemical Calculations? Journal of Physical Chemistry B 114 (2): 1191-1203 2010. DOI: 10.1021/jp910788e
[urlnadstranka] => [ogobrazek] => [pozadi] => [poduzel] => Array ( ) [iduzel] => 30219 [canonical_url] => [skupina_www] => Array ( ) [url] => /cheminf/publikace [sablona] => stdClass Object ( [class] => stranka [html] => [css] => [js] => [autonomni] => 1 ) ) [28306] => stdClass Object ( [obsah] => [poduzel] => Array ( ) [iduzel] => 28306 [canonical_url] => [skupina_www] => Array ( ) [url] => [sablona] => stdClass Object ( [class] => slider [html] => [css] => [js] => [autonomni] => 0 ) ) ) [sablona] => stdClass Object ( [class] => stranka [html] => [css] => [js] => [autonomni] => 1 ) [api_suffix] => )